نوترکیبی: نرعقیمی سیتوپلاسمی و برگرداندن باروری در گیاهان برتر(بخش سوم و پایانی)
3.2 عملکرد ژنهای PPR بعنوان ژنهای برگرداننده
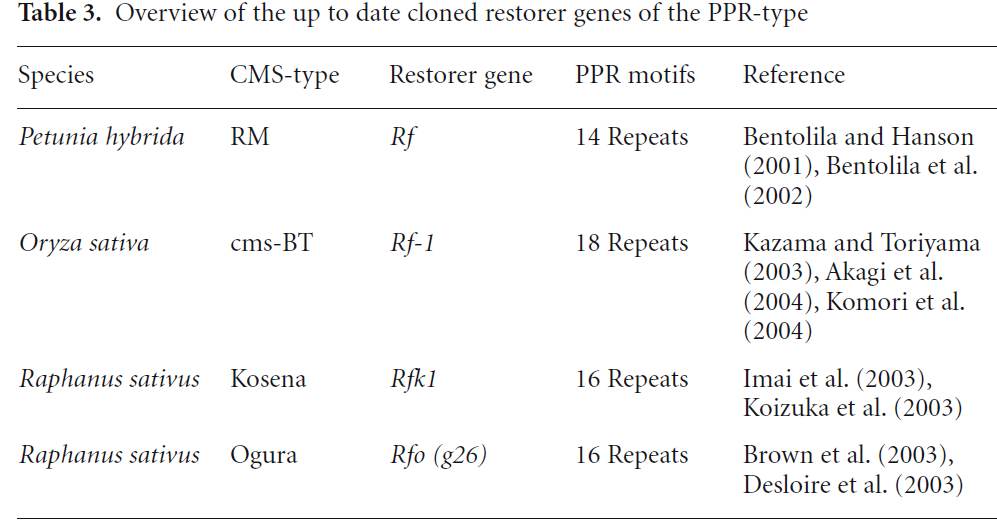
همه ژنهای ایزوله شده برگرداننده باروری، به استثنای ژن Rf2 ذرت، متعلق به خانوادهای از ژنها هستند که حاوی یک موتیف تکراری pentatricopeptide) PPR) هستند(جدول3). پروتئینهای حامل موتیفPPR، آرایشی متوالی از تکرارهای یک موتیف نزول یافته 35 آمینواسیدی را نشان میدهند. درArabidopsis.thaliana، بوسیله یک خانواده ژنی 450 عضوی، پروتئینهای حاوی PPR با تعداد تکرار 2 تا 26، رمز شدهاند. عمده این پروتئینها حدس زده میشود که مورد هدف میتوکندری یا کلروپلاست باشند. گمان میرود که پروتئینهای PPR بطور اختصاصی با RNA در اندامکها برهمکنش دارند و در پردازش یا ترجمه RNA نقش بازی میکنند.
نخستین ژن برگرداننده باروری از نوع PPR، از گیاه اطلسی جداسازی و کلون شد. براساس تکنیکهای مارکر مولکولی، ناحیه ژنومی حاوی ژن برگرداننده، به یک BIBAC با اندازه 37.5 kb محدود شده بود. سپس روشهای ترنس ژنیک برای شناسایی ژن برگرداننده از میان ژنهای کاندید مورد استفاده قرار گرفتند. ژن برگرداننده 592 اسید آمینه را کد میکند و بواسطه یک سیگنال متوالی از میتوکندری کنترل میشود. Rf-PPR592 باروری را به گیاهان ترنس ژنیک حامل سیتوپلاسم اطلسی برگردانده است. فراوانی پروتئین PCF مرتبط با CMS، بطور قابل ملاحظهای در این گیاهان کاهش مییابد. Rf-PPR592 حاوی 14 کپی از موتیف pentatricopeptide است و شامل 87 درصد از ناحیه رمز گذار میشود. لوکوس Rf در اطلسی ساختار ژنومی پیچیدهای را نشان میدهد و شامل یک ژن ثانویه (Rf-PPR591).PPR رمز گذار یک پروتئین 591 اسید آمینهای با عملکرد نامعلوم است. در مقایسه با Rf-PPR592، ژن همولوگ در لاینهای rf/rf دارای یک حذف در ناحیه پروموتر بوده و متفاوت از نظر توالی پیش بینی شده اسید آمینه است.
در برنج، نرعقیمی cms-BT (cms-bo) بواسطه حضور ژن غیرنرمال (B-atp6) atp6در ژنوم میتوکندری است. B-atp6 بصورت یک نسخه 2 کیلوبازی رونویسی میشود که علاوه بر atp6، حاوی یک توالی منحصر به فرد از orf79 در ناحیه '3 ژن atp6 است. در حضور ژن برگرداننده Rf-1، دو نسخه 1.5 و 0.45 kb بوسیله پردازش نسخه 2.0 kb بوجود میآیند. آنالیز توالی cDNA ثابت میکند که B-atp6-RNA پردازش شده بطور موثری بصورت N-atp6-RNA ویرایش شده است. ژن Rf-1 بنظر میرسد که در پردازش سهیم است وهمچنین بر فرایند ویرایش پس از ترجمه atp6 تأثیر دارد. برخی گروههای تحقیقاتی اقدام به کلون کردن ژن Rf-1 بوسیله ترکیب یک استراتژی کلونینگ براساس نقشه یابی و یک رویکرد مبتنی بر ژن کاندید کردهاند. نخستین بار در سال2003 ژن PPR8-1، رمزگذار یک پروتئینPPR، بعنوان ژن کاندید برای Rf-1، شناسایی شد. با استفاده از یک رویکرد ترنس ژنیک، ثابت شد که این نسخههای ژنی در پردازش نسخههای atp6 نقش دارند. پروتئین کد شده بوسیله PPR8-1، به تشکیل 0.45 kb RNA از رونوشت ژن B-atp6، به همان نحو که در موردRf-1 حدس زده میشود، کمک میکند. اما، این مسئله که آیا معرفی (واردسازی) PPR8-1 سبب باروری گیاهان باززایی شده میشود یا خیر، بررسی نشده است. PPR791 (Rf-1) که متعاقب یک استراتژی نقشه یابی دقیق کلون شده است همانند PPR8 است. ژن Rf-1 حدس زده میشود که یک پروتئین 791 اسید آمینهای، حاوی 16 موتیفPPR، را رمز میکند که از این بین، 14 موتیف پشت سرهم قرار دارند. به سبب حذف 1-bpدر ناحیه رمز گذار توافقی آلل مغلوب (rf-1) که منجر به frame shift و تولید زودهنگام کدون توقف میشود، این ژن یک پروتئین کوتاه شده 266 آمینو اسیدی، را رمز میکند. حذف 574 bp حاضر در ناحیه '3 توالی رمز کننده، احتمالاً بر عملکرد ژن برگرداننده تأثیری ندارد.
در کلزا یک ژن برگرداننده از نوع PPR برای Ogura-CMS و Kosena-CMS ایزوله شده است. ژن Rfo حاصل از Raphanus میتواند نرباروری را به کلزای حاوی سیتوپلاسم Ogura برگرداند. برخلاف Rf اطلسی، Rfo بر نسخههای متناظر با ژن میتوکندریایی مرتبط با نرعقیمی سیتوپلاسمی،orf138 ، تأثیری ندارد. Rfo در میزان ترجمه یا پس ترجمه تأثیر داشته و منجر به کاهش محصول ژن orf138 در برگها و گلها میشود. کلونینگ ژن Rfo بواسطه کاربرد synteny (روابط ژنومی) میان Raphanus و Arabidopsis تسهیل میشود، اگرچه Arabidopsis یک ژن PPR متناظر با ژن برگرداننده Rfo ندارد. ژنg26، رمز کننده یک پروتئین 687 اسید آمینهای با یک توالی پیش بینی شده هدف گذار میتوکندریایی، بعنوان ژن کاندید برای Rfo شناسایی شده است.
ژنهای در برگیرنده، g24 و g27، حاوی موتیفهای چندگانه PPR هستند، اما هر دو فاقد سومین تکرار g26 هستند. پروتئینهای پیش بینی شده رمز شده بوسیله این سه ژن از نظر طول مشابه هستند، g24p و g27p به ترتیب687 و654 اسید آمینه دارند در حالیکه محصول ژن Rfo(g26p) دارای687 اسید آمینه است. ترنسفورماسیون با استفاده از یک کلون حاوی g26، سبب تولید گیاهان باززایی شده بارور گردید. همچنین سه ژنPprA،PprB :PPR و PprC بر تربچه BAC-clone 64 یافت شدهاند. آنالیز توالی PprC پیشنهاد میکند که PprC یک ژن کاذب است. بطور خلاصه، Rfo احتمالاً متناظر با PprA یا PprB و یا هردو است.
آنالیز CMS میتوکندریایی تربچه Kosena نشان میدهد که Kosena حامل orf125 است که یک پروتئین 17-kDa را رمز میکند و حاوی توالی همولوگ با orf138، بجز دو آمینو اسید جایگزین و یک حذف 39-bp در ناحیه رمز کنندهorf138، است. تجمع ORF125 و ORF138 مرتبط با فنوتیپ CMS در Brassicaاست. ژن Rf بیان پروتئین در سطح ترجمه را تنظیم میکند. دو لوکوس هستهای Rfk1 و Rfk2، با آللهای غالب قادر به برگرداندن باروری به تربچه Kosena دارای سیتوپلاسم نرعقیم هستند. اگرچه میزان رونویسی orf125 در حضور آلل غالب Rfk1 تغییر نمیکند، تجمع پروتئین ORF125 بطور قابل توجهی کاهش مییابد. براساس استراتژی کلونینگ موضعی، ناحیه لوکوس برگرداننده باروری Rfk1 محدود به 43-kb در تربچه Kosena است که بوسیله چهار کلون lambda و یک کلون کاسمید پوشانده شده است. برای شناسایی Rfk1، زیر کلونهای حاوی ناحیه 43-kb از طریق ترنسفورماسیون با Agrobacterium بدرون لاین سیتوپلاسم نرعقیم B. napus وارد شدند. orf687 که 687 اسید آمینه با وزن مولکولی 76.5 kDa را رمز میکند بعنوان Rfk1 شناخته شده بود. آلل مغلوب حاوی 11 باز جایگزین است. پنج باز جایگزین، که سبب تولید چهار اسید آمینه جایگزین میشوند، همگی در ناحیه تکرارهای PPR واقع شدهاند. توالی پروتئین ORF687 رمز شده بوسیله Rfk1 مشابه پروتئین g26p است. بنابراین، اگرچه تفاوتهایی از نظر شاخصههای سیتوپلاسم نرعقیم میتوکندریایی میان سیتوپلاسم Kosena و Ogura تربچه وجود دارد، بازگشت باروری به هر دو سیستم میتواند بوسیله ژنهای رمز کننده پلی پپتید یکسان انجام شود.
این امر که بسیاری از ژنهای برگرداننده، موتیفهای PPR را نشان میدهند بطور قابل توجهی ایزوله کردن ژنهای کاندید برای ژنهای برگرداننده را در دیگر گونهها تسهیل میکند.
4. نتیجه گیری
عملکرد میتوکندری مشخصاً برای رشد دانه گرده حیاتی است. سیستمهای CMS و ژنهای متناظر برگرداننده باروری، امکانات مناسبی برای مطالعه نقش میتوکندری در رشد گرده و برهمکنش هستهها و میتوکندری در این رابطه را ارائه میکنند. اگرچه عوامل نرعقیمی سیتوپلاسمی با جزئیات در سطح مولکولی، مطالعه شدهاند ایزولاسیون ژنهای برگرداننده تنها شروع شده است. شناسایی ژنهای برگرداننده متعلق به خانواده ژنی PPR ممکن است احتمال پیشرفت بهتر در کلونینگ آتی ژنهای برگرداننده را بوسیله ترکیب کلونینگ برپایه نقشه یابی با رویکردهای ژن کاندید را میسر سازد. با این همه، تنها آینده نشان خواهد داد که آیا تمامی ژنهای برگرداننده متعلق به یک نوع مشابه هستند و یا اینکه دیگر انواع ژنهای برگرداننده مشخص خواهند شد. برای این ژنها، فرآیند کلونینگ طولانیتر خواهد بود و سیستمهای ترنس پوزون- تگ گذاری، بعنوان جایگزینی برای استراتژی کاربرد کلونینگ برپایه نقشه یابی، برای تمامی گیاهان میسر نیستند. اگرچه چارچوبهای خواندن باز مرتبط با CMS و پروتئینهای رمز شده شناسایی شدهاند عملکرد و نقش این پروتئینها، صرف نظر از پروتئین T-URF13 ذرت، هنوز معلوم نشده است. ایزولاسیون و مطالعه عملکرد ژن برگرداننده ممکن است فهم بهتر فرآیندهای دخیل را میسر سازد. اما، بطور کلی بنظر میرسد که هر گونه اختلال در عملکرد میتوکندری، برای فرآیند به شدت انرژی خواه رشد دانه گرده در گیاهان برتر، مرگبار خواهد بود.
برای آنالیز مولکولی نرعقیمی سیتوپلاسمی و بازگشت باروری، مارکرهای مولکولی مناسبی ارائه شده است که انگشت نگاری هیبریدها و ارزیابی خلوص بذور هیبرید بمنظور کاربردهای تجاری، را برپایه استراتژیهای مبتنی بر PCR میسر میسازد.
این مطلب، ترجمهای از مقاله:
" Recombination:Cytoplasmic male sterility and fertility restoration in higher plants"
نوشته Renate Horn(2006) بود، جهت دانلود متن اصلی مقاله، به همراه منابع آن، بر روی لینک زیر کلیک فرمایید:
http://s1.picofile.com/file/7545474408/CMS_Rf.pdf.html
نوترکیبی: نرعقیمی سیتوپلاسمی و برگرداندن باروری در گیاهان برتر(بخش اول)
نوترکیبی: نرعقیمی سیتوپلاسمی و برگرداندن باروری در گیاهان برتر(بخش دوم)
برچسبها: نوترکیبی, نرعقیمی سیتوپلاسمی و ژنهای برگرداننده باروری


